
时间管理下的学习方法!——科研狗需要知道的十大高效经验(1)
2020年2月17日
InVisor科研新闻 | 传奇“夜光杯”材料精准定位癌细胞,看你还往哪里跑!
2020年3月2日InVisor科研新闻 | 新型冠状病毒你等着!新方法测你RNA的序分分钟的事儿!!

2020年魔障了。
突如其来的新冠病毒不仅其变态的传播性让所有人都为之色变,惶恐不宁,还于短短三周内暴露了灿烂阳光下的发指“罪恶”,和谐社会下的惨淡“人性”。2003年出生的孩子们在被SARS袭扰后,哪知今日又面临着新冠的恐吓,或多或少地影响了他们的高考,他们的未来走向。
假期延长,宅家良久,国家经济受损,小微企业重创,多少烦心事也让头发生长速度变快,不知不觉在镜子中照见了杀马特的自己,却无处可寻理发店修理。
经此一“疫”,芳老师越发尊敬医生、警察、老师,也不知是从哪儿瞟来的一句话,说,救人之士,护国之侍,育人之师总是可以在危难中挽救社会。嗯,很有道理。这其中的老师当然不只包括培养出医生、警察的老师,还包括奋战一线,攻克难题的科学家,他们也是保障社会的中坚力量。这次疫情,他们也在国家背后奉献出自己的智慧,想尽办法打败这次的病毒。其中,北大和清华,强强联手的课题组最近的成果有望助力新冠病毒的测序工作,因为他们发明出了一种全新的方法可以在测序前加快建库速度,节省了大量时间和成本,破解新冠病毒以及其他生物信息的秘密更快了一步。

这一方法被命名为“SHERRY”(想到了可爱的灰原哀哀酱~),全称为Sequencing HEteRo RNA-DNA-hYbrid,研究团队的谢晓亮教授很有情趣哈,算上前面MALBAC和LIANTI,这已经是第三次用酒的名字给新发明的方法命名了(有种柯南黑衣组织酒厂的既视感……)。
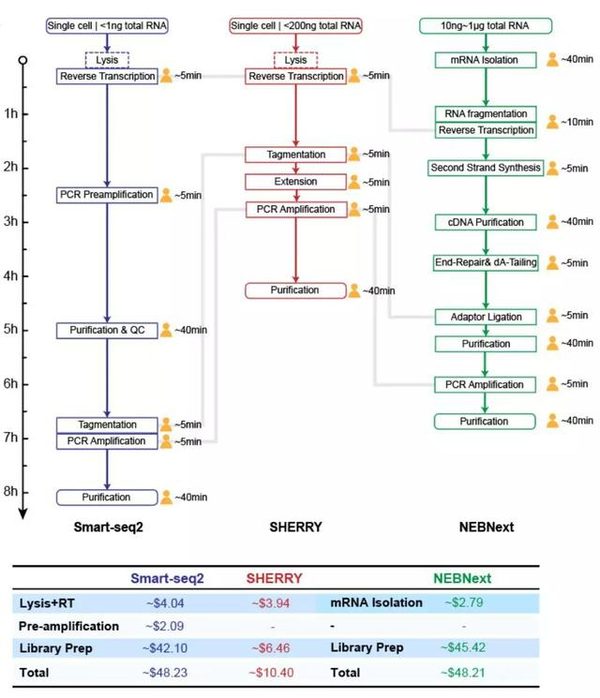
SHERRY方法核心在于Tn5转座酶,说到这儿芳老师扯远一点聊一聊如果要测一段RNA的序列应该怎么测,也算是给入门研究的萌新们做一个简单的介绍吧。
传统RNA测序方法,也叫做Smart-seq2方法,其步骤非常复杂且繁琐,首先你要将RNA从细胞等生物单体或病毒等类生物中分离出来,这一部分就要分情况而采用不同的方法了,因为像真核生物中的RNA不像RNA病毒那样直接为主要遗传物,不同生命RNA含量也有差异。如果是测真核生物的RNA,那我们主要选用mRNA,因为大家都知道,咱们真核生物中RNA有多种,其中大家熟悉的rRNA“独占八斗”,占RNA总含量的85%左右。但是它多不一定有用,rRNA也叫核糖体RNA,是核糖体重要组成部分,而核糖体又是将mRNA上的信息转化为实实在在的肽链的,这一“翻译”的角色就注定它不能改变多少,必须保持稳定,不然整个“转录翻译”这一维持生物正常运作的过程就乱套了。mRNA又是由DNA转录来的,上面携带的生物信息跟DNA息息相关,所以,虽然mRNA只占RNA含量的3%,但信息含量大,非常值得我们研究。
实验中,首先我们要做的就是富集mRNA,并去除掉rRNA以及其他RNA,一般采用的方法是Oligo(dT)特异分离方法。Oligo(dT)引物是一段只有胸腺嘧啶组成的核苷酸链,而它能够特异地结合到mRNA尾部的Poly(A)上,然后把mRNA从“万军丛中”拉出来。不过此时我们分离出来的mRNA是搅成一团的,而且很长,不太好测序,于是我们接下来就要将mRNA随机打碎(Tagmentation),形成一小段一小段的序列,这些序列可以作为接下来cDNA的反转录模板。cDNA也叫互补脱氧核糖核酸,我们用逆转录酶将打碎的mRNA片段给“还原”成DNA,随后给这些反转录好的cDNA加接头(Adapter),让DNA聚合酶识别到并且把某一cDNA进行扩增,也就是将其放大数百万倍,形成重复的一长串DNA,方便我们随后的分析与检测。这里通常是用PCR(Polymerase chain reaction)扩增,这一技术应用广泛,像犯罪取证、亲子鉴定、考古学等等都会用到。等到我们得到了想获取的DNA长串后,就可以构建文库,上机测序了。
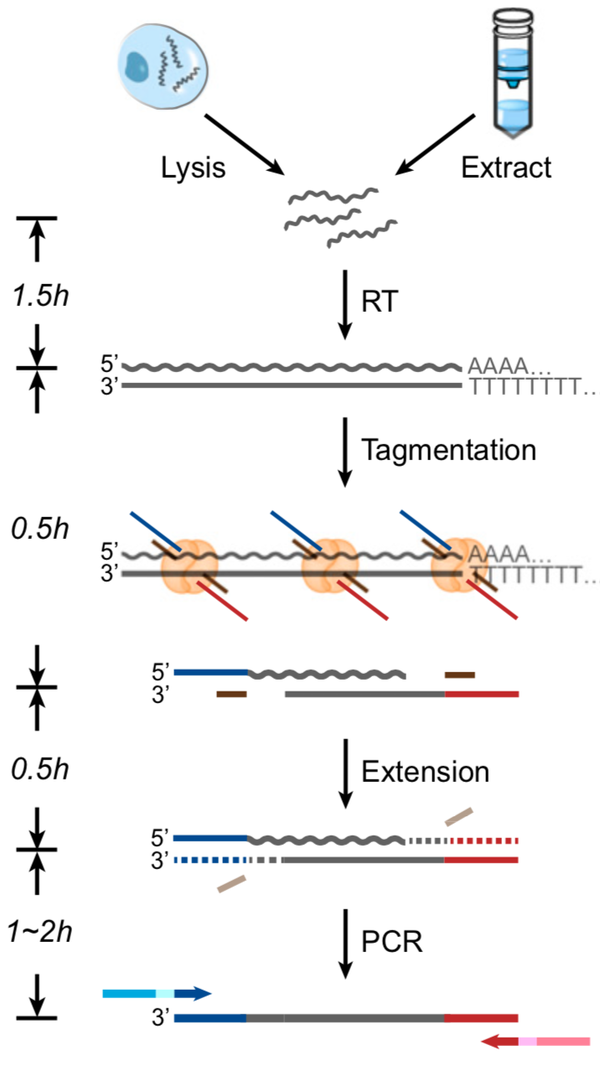
不过用Tn5转座酶就省事儿多了,Tn5转座酶之所以被看中是因为它非常“粗暴且干脆”,能在一步内完成多步的事情:打断DNA并直接给DNA接上接头。研究团队一看,我靠,那么我直接把Tn5转座酶放到RNA和DNA的混合链中,岂不是一步到位?这样我在用Oligo(dT)把mRNA分离出来的时候,直接将其反转录,然后把Tn5转座酶放进去,一口气打断RNA和DNA的混合链并将其接上接头,这大大节省了在传统建库中还必需的cDNA以及扩增等等步骤,简直不要太爽!
经研究团队统计及分析,由于SHERRY方法仅在一根试管中就可以完成,其耗时相比于Smart-seq2的实验时间足足减少了一半!总共耗费的时间大约在3.5~4.5h之间,人工操作花费时间更是只有半个钟头!并且SHERRY耗材少,比Smart-seq2法少耗五分之四的实验用材,且规避了PCR扩增法中对高CG含量的基因扩增效率低下所导致的偏向性问题,每一个科研狗用了都说好~(流下了感动的泪水!!)
北大谢晓亮教授还非常鼓励将这种方法运用到新冠病毒的测序中,虽然这是第一次临床测序,但SHERRY方法比现有的RNA测序更简单,更高效,对于新冠病毒这类传播快,变异率高的病毒非常重要。芳老师又多了一个敬佩的人儿吼!!!
当然,这次实验也被团队中北大博士研究生狄琳和傅语思写成名为《RNA sequencing by direct tagmentation of RNA/DNA hybrids》的论文,发表在国际权威学术期刊《美国科学院院刊》上。
p.s.《美国科学院院刊(PNAS,Proceedings of the National Academy of Sciences of the United States of America)》是于1915年由美国国家科学院出版的官方期刊,主要内容偏向于原创研究、科学评论等,2018年Impact Factor为9.58,自2008年来累计被引用次数超过170万次,是第二大被引用最多的期刊,广受读者和业内学者的好评。

最后,希望2021年大家都好好的!!一定一定哦!!!拉钩~
大家可以对InVisor芳老师多多支持哦~点赞点赞点赞哈!!!最后,如果大家对于「科研背景提升」、「论文发表」、「科研课题辅导」、「名校科研助理申请」有任何想法的话,欢迎来戳一戳芳老师(一般人不告诉ta的客服微信:invisor003,记得备注“学术科研”哈~~~)️❤️❤️
参考链接:北京大学生物医学前沿创新中心




